Was ist ein Genom?
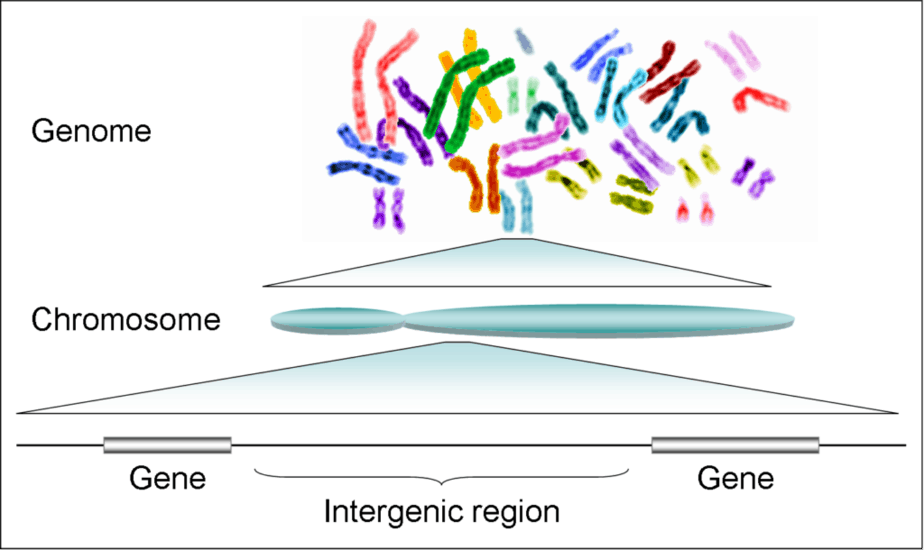
Das Genom ist das gesamte Material, das die Erbinformation einer Zelle oder eines Viruspartikels enthält. Es existiert als Chromosomen, DNA oder RNA im Fall von RNA-Viren. In einem abstrakten Sinne umfasst dies auch die Gesamtheit der Erbinformationen eines Individuums.
Der Begriff „Genom“ wurde 1920 von Hans Winkler geprägt. Die Genomforschung untersucht normalerweise strukturelle Variationen und die Wechselwirkungen zwischen diesen Gene .
Herausgegeben von Christina Swords, Ph.D.
Grundlagen
Die für die Vererbung von Merkmalen erforderlichen Informationen sind in der DNA enthalten. Insbesondere liegt es in der Sequenz der DNA-Basen Adenin (A), Guanin (G), Cytosin (C) und Thymin (T). Ribonukleinsäuren verwenden die Base Uracil (U) anstelle von Thymin. Nach der Regel des genetischen Codes bedeuten drei aufeinanderfolgende Basen jeweils eine Aminosäure.
Es wird zwischen codierenden und nicht codierenden DNA-Abschnitten unterschieden. Proteine werden aus Aminosäuren im Verlauf der Genexpression gemäß der Basensequenz der codierenden Abschnitte gebildet. Nichtkodierende Regionen können jedoch auch wichtige Funktionen haben, beispielsweise bei der Genregulation. Es gibt auch Pseudogene: Gene, die aufgrund von Mutationen funktionslos geworden sind und vom Organismus nicht mehr gelesen werden können.
Neben der DNA im Zellkern befindet sich in anderen Teilen der Zelle weiteres genetisches Material. In Eukaryoten finden sich in den Mitochondrien (Mitogenom, auch Chondriom) eigene kleine Genomsequenzen. In Algen und Landpflanzen kommen sie fast immer in Chloroplasten und anderen Plastiden (Plastomen) vor. Prokaryoten (Bakterien und Archaeen) enthalten häufig zusätzliche, relativ kurze, in sich geschlossene DNA-Moleküle, die als Plasmide bezeichnet werden.
Organisation von Genomen
Eukaryoten
Bei Eukaryoten besteht das Kerngenom (Karyom) aus mehreren bis zahlreichen strangartigen Chromosomen. Die Kern-DNA wird auch als Kern-DNA (nDNA) bezeichnet. Die Anzahl der Chromosomen ist speziesspezifisch und kann von zwei (beim Pferdewurm) bis zu mehreren hundert (bei einigen Farnen) variieren.
Die Anzahl der Chromosomen ändert sich auch, wenn sich die Kernphase ändert (Meiose und Karyogamie). Eukaryontische Genome haben auch einen hohen Anteil an nicht-kodierender DNA und die Intron-Exon-Struktur in ihren Genen.
Prokaryoten
In Prokaryoten liegt die DNA als langes, in sich geschlossenes Molekül vor. Darüber hinaus können kürzere, ebenfalls in sich geschlossene DNA-Moleküle, sogenannte Plasmide, in variabler Anzahl vorliegen. Diese können unabhängig von der Haupt-DNA amplifiziert und auch über Speziesgrenzen hinweg an andere prokaryotische Zellen (Konjugation) weitergegeben werden. Sie enthalten in der Regel nur wenige Gene, die beispielsweise eine Antibiotikaresistenz vermitteln.
Prokaryontische Genome sind im Allgemeinen viel kleiner als eukaryotische Genome. Sie enthalten relativ kleine nichtkodierende Teile (5-20%) und auch nur wenige oder keine Introns.
Organellen
Die Genome der Mitochondrien, Plastiden und anderer Arten von Hydrogenosomen sind wie Prokaryoten organisiert. Nach der endosymbiotischen Theorie wird angenommen, dass diese Organellen früher als frei lebende Prokaryoten existieren. Diese „Mitogenome“ und „Plastome“ enthalten auch einen kleinen Teil der Gene, die für ihre eigene Funktion benötigt werden. Deshalb werden diese Organellen als „halbautonom“ bezeichnet.
Viren
Virale Genome sind sehr klein, da sie nur wenige Proteine enthalten. Die genetische Information ist stark verdichtet, da sich verschiedene Gene überlappen. Einige Abschnitte können gleichzeitig auch als Gene in den Leserichtungen verschiedener Sequenzen fungieren. Das virale Genom (auch als Virom bekannt) kann
- bestehen aus DNA oder RNA,
- dies kann einzel- oder doppelsträngig sein,
- linear oder kreisförmig geschlossen sein und
- sind in mehrere Teile unterteilt (mehrteilig) oder unsegmentiert (einteilig)
Eine Besonderheit sind Retroviren. Ihr RNA-Genom kann durch reverse Transkription in DNA „übersetzt“ und in das Wirtsgenom integriert werden. Die Eigenschaften der Genome der Viren sind wichtige Kriterien für ihre Klassifizierung.
Einige Viren und insbesondere Virophagen (Viren, die andere Viren angreifen) haben mobile genetische Elemente (Transposons, Transpovirons, Polintons). Im Allgemeinen wird ihre Gesamtheit auch als Mobilom bezeichnet.
Viroide
Die genomische RNA von Viroiden ist kurz. Es erstreckt sich zwischen 241 und 401 Nukleotiden und enthält viele komplementäre Regionen, die doppelsträngige Sekundärstrukturen bilden. Viroide haben keine zusätzliche Hülle und sind 80- bis 100-mal kleiner als die kleinsten Viren. Sie vermehren sich in lebenden Zellen höherer Pflanzen.
Genomgrößen
Die Genomgröße ist die Menge an DNA, die in einem Genom vorhanden ist. Bei Eukaryoten bezieht sich diese Information normalerweise auf den haploiden Chromosomensatz, der auch als C-Wert bezeichnet wird. Es wird entweder die Anzahl der vorhandenen Basenpaare (bp) oder die DNA-Masse in der Einheit pg (Pikogramm) angegeben.
Ein pg doppelsträngiger DNA besteht aus etwa 0,978-109 bp, dh fast einer Milliarde Basenpaaren. Verschiedene Organismen haben unterschiedliche Pikogramme zu Basenpaarverhältnissen Trotzdem sind die beiden Einheiten nicht immer leicht zu vergleichen.
Mit der Leichtigkeit von Genomsequenzierung In den letzten zehn Jahren wurde häufiger die Genomgröße in Basenpaaren gemessen. Um 1.000 Basenpaare zu summieren, wird üblicherweise der Begriff „Kilobasenpaare“ (kbp oder kb) verwendet. Für eine Million Basenpaare verwenden wir „Megabasispaare“ (Mbp oder Mb).
1972 wurde der äthiopische Lungenfisch ( Protopterus aethiopicus ) wird oft als Wirbeltier mit dem größten Genom bezeichnet bei ungefähr 133 pg . Im Jahr 2014 wurde der Rekord von Heuschrecke gebrochen ( Locusta migratoria ) mit 6,3 Gbit / s . Im Jahr 2018 32 Milliarden Basenpaare wurden aus dem mexikanischen Axolotl nachgewiesen ( Ambystoma mexicanum ).

Der Blattfloh Endosymbiont Carsonella ruddii hat das kleinste quantifizierte Bakteriengenom in 2006 . Sein zirkuläres DNA-Molekül enthält nur etwa 160.000 Basenpaare, die alle Informationen enthalten, die es zum Leben benötigt.
Die DNA einer einzelnen menschlichen Zelle ist aneinandergereiht etwa 1,80 m lang. Theoretisch hat ein Basenpaar einen Informationsgehalt von 2 Bits, da es 4 Zustände annehmen kann (A / T / G / C). Mit ungefähr 3,27 Milliarden Basenpaaren würde sein maximaler Informationsgehalt 6,54 Milliarden Bits oder 780 MiB betragen.
Der tatsächliche Informationsgehalt ist vermutlich geringer, da große Teile der DNA nichtkodierende Sequenzen mit partiellen regulatorischen Funktionen enthalten. Laut dem Ergebnisse des Humangenomprojekts 2003 enthielten 99,99% des menschlichen Genoms Gene.
Es besteht ein Mangel an Korrelation zwischen der Genomgröße und der Komplexität des Organismus oder dem „C-Wert-Paradoxon“. Zum Beispiel haben Caudate ein größeres Genom als Reptilien, Vögel und Säugetiere. Lungenfische und Knorpelfische haben ein größeres Genom als echte Knochenfische. Innerhalb von Blütenpflanzen oder Protozoen variiert die Genomgröße jedoch erheblich.
Die größte Menge an DNA findet sich in einfachen Eukaryoten wie Amöben und Urfarnen. Diese Organismen haben ungefähr eine Billion Basenpaare. Ihr Genom enthält auch einzelne Gene als tausendfache Kopien und lange nicht proteinkodierende Abschnitte.
