Inhaltsverzeichnis
- Was ist die Sequenzierung des gesamten Exoms?
- Durchführen einer Sequenzierung des gesamten Exoms
- Wer sollte getestet werden?
- Vorteile der Sequenzierung des gesamten Exoms
- Einschränkungen der Sequenzierung des gesamten Exoms
- Chromosomaler Microarray vs. Sequenzierung des gesamten Exoms vs. Sequenzierung des gesamten Genoms
- Direkt an den gesamten Exom-Sequenzer der Verbraucher
Was ist die Sequenzierung des gesamten Exoms?
Die vollständige Exomsequenzierung (WES) ist die Sequenzierung des Exoms, aller proteinkodierenden Gene im Genom. Die gesamte Exomsequenzierung umfasst zwei Schritte. Der erste Schritt besteht darin, Sequenzen nur im menschlichen Exom anzuvisieren. In der Humangenetik sind diese Zielregionen etwa 60 Millionen Basenpaare oder etwa 1% des menschlichen Referenzgenoms. Der zweite Schritt besteht darin, die DNA unter Verwendung einer beliebigen DNA-Sequenzierungsplattform mit hohem Durchsatz zu sequenzieren und die Ergebnisse zu analysieren.
Die Exomsequenzierung ermöglicht es, genetische Veränderungen zu erkennen, die zu Veränderungen der Proteinsequenzen führen, die wiederum zu Krankheiten wie z Atherosklerose , Alzheimer-Erkrankung , und andere. Viele Krankheiten treten in der Protein-kodierenden Region des Genoms auf, und dieser Prozess ermöglicht es Benutzern, mehr über ihre Veranlagung für Krankheiten zu erfahren als die Analyse einzelner Gene. Es ist jedoch jetzt bekannt, dass DNA-Variationen außerhalb der Exons die Genaktivität und Proteinproduktion beeinflussen und auch zu genetischen Störungen führen können. Eine vollständige Exomsequenzierung würde diese Variationen übersehen.
In der Vergangenheit war der Hauptvorteil der Exomsequenzierung die Fähigkeit, ein besseres Genscreening durchzuführen und krankheitsassoziierte Mutationen wie Kopienzahlvarianten auf eine Weise nachzuweisen, die kostengünstig war und weniger Zeit in Anspruch nahm als die Sequenzierung des gesamten Genoms. Dank der Fortschritte in der Sequenzierungstechnologie ist die Sequenzierung des gesamten Genoms jetzt genauso schnell und genauso erschwinglich. Nebula Genomics bietet die günstigste 30-fache Sequenzierung des gesamten Genoms für 299 US-Dollar oder weniger. Wir dekodieren 100% Ihrer DNA, nicht nur 1% wie bei der Sequenzierung des gesamten Exoms, um Ihnen die umfassendste Ansicht Ihrer DNA zu bieten.
Durchführen einer Sequenzierung des gesamten Exoms
Die Sequenzierung des gesamten Exoms beginnt mit der DNA-Isolierung und -Anreicherung und endet mit der DNA-Sequenzierung und -Analyse.
Strategien zur DNA-Isolierung und -Anreicherung
DNA wird aus einer bereitgestellten Probe wie einer Speichelprobe oder einem Wangenabstrich isoliert. Die häufigste Form der DNA-Isolierung ist die Phenol-Chloroform-Extraktion.
Es gibt verschiedene Strategien, um DNA aus Proben anzureichern. Die verwendete Methode hängt häufig von der Probe und dem gewünschten Ergebnis ab.
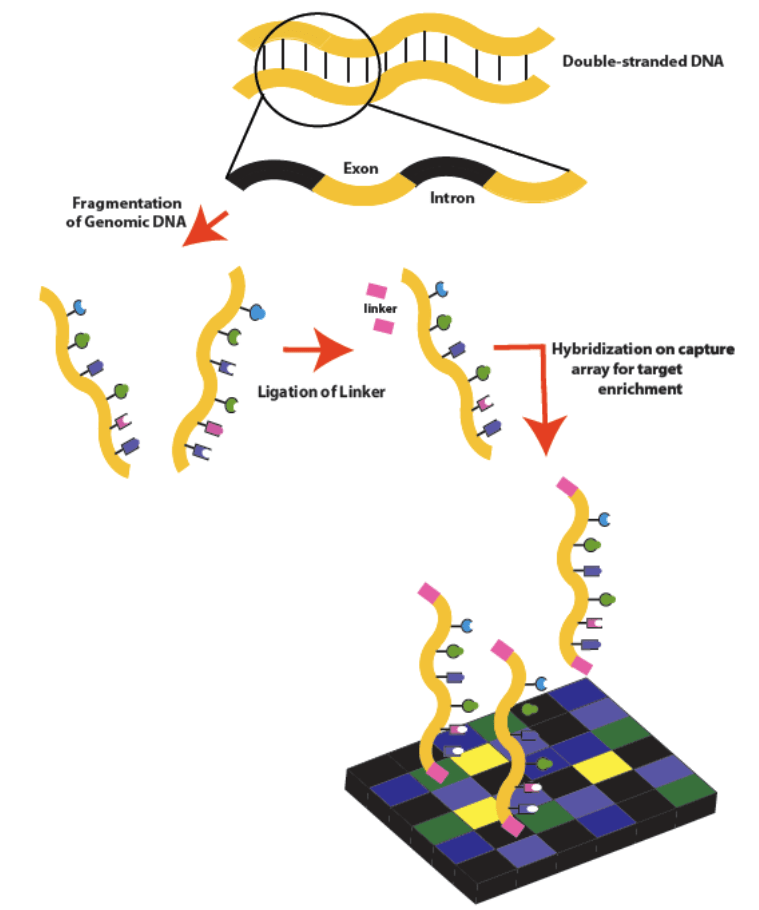
- PCR: Die Polymerasekettenreaktion (PCR) ist der häufigste Weg, um gewünschte DNA-Fragmente für die Sequenzierung zu amplifizieren.
- Molekulare Inversion: Bei dieser Methode wird der interessierende Bereich in einem Ring geschlossen. Ein einzelsträngiger DNA-Oligonukleotidprimer enthält einen zentralen Teil mit einer universellen Sequenz mit Restriktionsstellen, während die Enden zu den beiden Abschnitten genomischer DNA komplementär sind, zwischen denen sich die interessierende Sequenz befindet.
- Hybridisierung, Array-basiertes Capture: Es werden Microarrays verwendet, die einzelsträngige Oligonukleotide enthalten, die an ein Substrat gebunden sind, mit Sequenzen aus dem Genom, die die interessierenden Stellen abdecken können. Genomische DNA wird in Fragmente geschnitten, die Enden der Fragmente werden stumpf gemacht und Universalprimer werden hinzugefügt. Nach der Hybridisierung der Fragmente mit Sonden auf Microarrays werden die nicht hybridisierten Fragmente vom Substrat gewaschen und die verbleibenden Fragmente werden dann mittels PCR amplifiziert
- Einfangen in Lösung: Ein Satz Sonden wird in Lösung synthetisiert und auf Streptavidinperlen fixiert. Die Kügelchen werden in eine Lösung mit fragmentierter genomischer DNA gegeben, wobei die Sonden selektiv an die gewünschten genomischen Stellen hybridisiert werden, wonach die Kügelchen mit den interessierenden Fragmenten ausgefällt und gewaschen werden. Die Abschnitte werden dann sequenziert.
DNA-Sequenzierung
Da sind viele Next Generation Sequencing (NGS) Technologieplattformen verfügbar. Einige umfassen den Roche 454-Sequenzer und die SOLiD-Systeme von Life Technologies, den Life Technologies Ion Torrent und Illuminas Illumina Genome Analyzer II (nicht mehr verfügbar) sowie nachfolgende Instrumente der Serien Illumina MiSeq, HiSeq und NovaSeq. „Kurz gelesen“ NGS-Systeme sind ideal für die Analyse vieler relativ kurzer Abschnitte der DNA-Sequenz, wie sie im Exom zu finden sind.
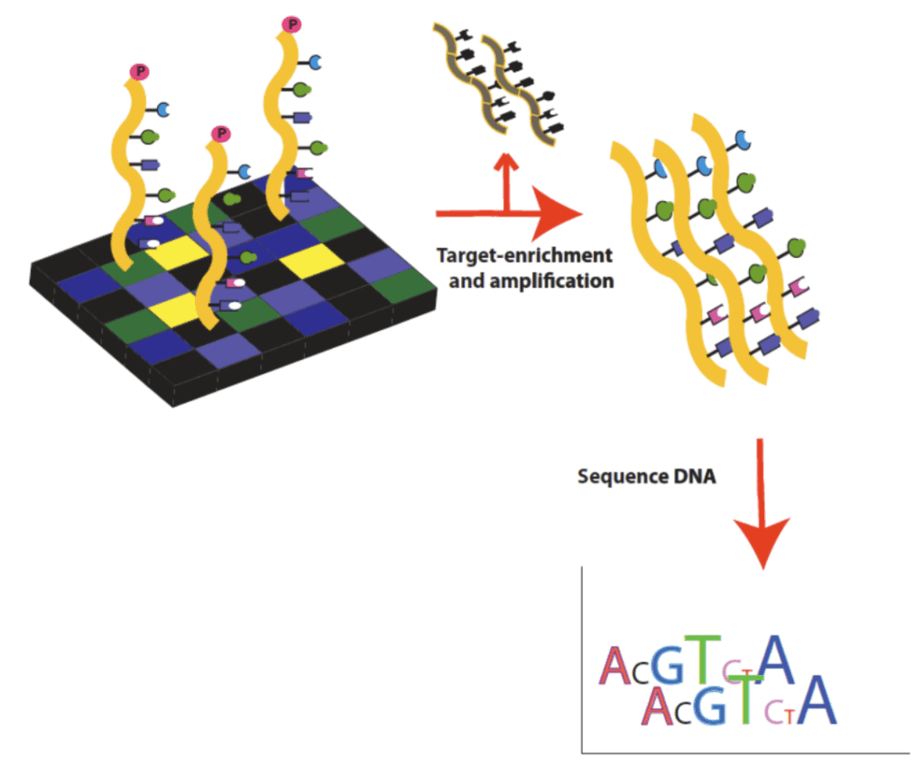
Datenanalyse
Selbst die Sequenzierung von nur 1% des menschlichen Genoms erzeugt viele Exomsequenzierungsdaten und erfordert eine umfangreiche Datenanalyse, für die es zahlreiche Programme zum Ausrichten und Zusammenstellen von Sequenzlesungen gibt. Einige Strategien zur Verbesserung der Qualität der Datengenerierung umfassen:
- Vergleich der identifizierten genetischen Varianten zwischen Sequenzierung und Array-basierter Genotypisierung (falls möglich)
- Vergleich der codierenden SNPs mit einem gesamten Genom sequenzierten Individuum mit der Störung
- Vergleich der codierenden SNPs mit der Sanger-Sequenzierung von HapMap-Individuen
Erschaffen Variantenaufrufe Analyseprogramme identifizieren Varianten aus Sequenzdaten, um verschiedene Dateien zu erstellen. Einige der gängigen Dateien sind FASTQ-, BAM / CRAM- und VCF-Dateien.
Sie können mehr über das gesamte Exomsequenzierungsverfahren über die gesamte Exomsequenzierung lesen Wiki-Seite .
Wer sollte getestet werden?
Das Amerikanisches College für Medizinische Genetik und Genomik hat Richtlinien darüber, wann Sequenzierungsmethoden verwendet werden sollten, welche Ergebnisse auftreten können und was die Ergebnisse anzeigen könnten.
Insbesondere empfehlen sie, Gentests für bestimmte Personen in Betracht zu ziehen, darunter:
- Die Daten zum Phänotyp oder zur Familiengeschichte implizieren stark eine genetische Ätiologie, aber der Phänotyp entspricht nicht einer bestimmten Störung, für die klinisch ein Gentest verfügbar ist, der auf ein bestimmtes Gen abzielt
- Ein Patient weist eine definierte genetische Störung auf, die ein hohes Maß an genetischer Heterogenität aufweist, was die WES- oder WGS-Analyse mehrerer Gene gleichzeitig zu einem praktischeren Ansatz macht
- Ein Patient weist eine wahrscheinliche genetische Störung auf, aber spezifische genetische Tests, die für diesen Phänotyp verfügbar sind, haben keine Diagnose erhalten
- Ein Fötus mit einer wahrscheinlichen genetischen Störung, bei der bestimmte Gentests durchgeführt werden
Vorteile der Sequenzierung des gesamten Exoms
Ganze Exom-Sequenzierungstechnologie, wie andere auch DNA-Testmethoden zielt darauf ab, das Genom zur Diagnose und Anleitung von Behandlungen für Mendelsche Erkrankungen zu verwenden. Außerdem erhalten Benutzer Informationen, mit denen sie Familienmitglieder über ihr Risiko informieren können.
Diese Methode hat mehrere Vorteile gegenüber der Einzelgenanalyse, einer der häufigsten Methoden zur DNA-Sequenzierung. Erstens bietet die Sequenzierung des gesamten Exoms die Möglichkeit, eine breite Palette von Mutationen in Kandidatengenen zu identifizieren, die nicht getestet wurden. Auf diese Weise kann ein Benutzer Krankheitsgene identifizieren, von denen er möglicherweise nicht vermutet hat, dass sie einem Risiko ausgesetzt sind. Zweitens bietet die Sequenzierung des gesamten Exoms in der Klinik die Möglichkeit, Fälle zu identifizieren, in denen Mutationen aus verschiedenen Genen zu den verschiedenen Phänotypen bei demselben Patienten beitragen.
Die vollständige Exomsequenzierung kann auch in der wissenschaftlichen Forschung verwendet werden, um seltene Erbkrankheiten zu identifizieren, die von Microarrays nicht erkannt werden können. Beispielsweise ist bekannt, dass sich die Allelvarianten für mehrere schwere Erkrankungen auf den Exons befinden, aber auch in der Bevölkerung äußerst selten sind. Daher fehlen bei Standard-Genotypisierungstests, für deren Wirksamkeit große Alleldatenbanken erforderlich sind, diese Varianten häufig. Mehrere Fallstudien unterstreichen die Nützlichkeit des gesamten Exomsequenzierungsansatzes. Im Jahr 2009 wurde eine Gruppe von Wissenschaftler verwendeten die Sequenzierung des gesamten Exoms, um die Mutation zu identifizieren, die das Bartter-Syndrom und angeborenen Chloriddurchfall verursacht.
Im Jahr 2011 war Ambry Genetics die erste Firma einen Exomsequenzierungsdienst für die Diagnose klinischer Krankheiten anzubieten. Das Unternehmen behauptet, dass die Ergebnisse der Exomsequenzierung es ihnen ermöglichen werden, Krankheiten zu diagnostizieren, für die herkömmliche diagnostische Ansätze nicht anwendbar sind. Sie können mehr über die Geschichte und die Ergebnisse von lesen Ambry Genetics in unserer Produktbewertung!

Einschränkungen der Sequenzierung des gesamten Exoms
Sequenzierung des gesamten Exoms und Sequenzierung des gesamten Genoms : Beide Verfahren sind Sequenzierungstechnologien der nächsten Generation. Die Sequenzierung des gesamten Exoms zeigt zwar einige Vorteile gegenüber der Microarray-basierten Genotypisierung für die klinische Analyse des Krankheitsrisikos, weist jedoch auch Einschränkungen auf. Der wichtigste Unterschied zwischen der Sequenzierung des gesamten Exoms und des gesamten Genoms ist die Menge der sequenzierten DNA. Da die Sequenzierung des gesamten Exoms nur 1% des Genoms dekodiert, können die anderen 99%, einschließlich struktureller und nicht kodierender Regionen, nicht analysiert werden. Auf der anderen Seite zeigt die Gesamtgenomsequenzierung die gesamten 100% Ihrer DNA, die alle 3 Milliarden Basenpaare enthält (nur 40 Millionen Basenpaare sind mit der gesamten Exomsequenzierung abgedeckt).
Wie viel kostet die Sequenzierung des gesamten Exoms? Für eine Weile wurde die Sequenzierung des gesamten Exoms als die vorteilhafteste Art der DNA-Sequenzierung angesehen, da sie eine erweiterte Ansicht der DNA-kodierenden Regionen im Vergleich zur Microarray-Genotypisierung zu einem viel niedrigeren Preis als die Sequenzierung des gesamten Genoms bot. Dies ist jedoch nicht mehr der Fall.
Die Sequenzierung des gesamten Genoms kann zu einem Bruchteil des ursprünglichen Preises erreicht werden und liefert mehr Informationen als die Sequenzierung des gesamten Exoms. Beim Nebula Genomics können Sie Ihr gesamtes Genom für weniger als 299 US-Dollar sequenzieren lassen. Dies ist vergleichbar und sogar billiger als viele Heim-Exom-Sequenzierungsprodukte.
Chromosomaler Microarray vs. Sequenzierung des gesamten Exoms vs. Sequenzierung des gesamten Genoms
| Microarray-Genotypisierung | Sequenzierung des gesamten Exoms | Sequenzierung des gesamten Genoms | |
| Zweck | Identifizieren Sie bestimmte Varianten | Dekodiere alle Gene | Dekodieren Sie alle Gene sowie alle strukturellen und nicht kodierenden Regionen |
| Durchsatz | Niedriger Durchsatz | Hoher Durchsatz | Hoher Durchsatz |
| Erfordert die vorherige Identifizierung der Variante | Ja | Nein | Nein |
| Deckungsbetrag | 0,5 Millionen Positionen (0,02% des Genoms) | 60 Millionen Stellen (~ 1% des Genoms) | 6 Milliarden Stellen (~ 100% des Genoms) |
| Kosten | ~ 100 $ | ~ 300 $ | ~ 1000 $ (aber Nebula Genomics bietet es für 299 US-Dollar an) |
Direkt an den gesamten Exom-Sequenzer der Verbraucher
Verschiedene Unternehmen verkaufen ganze Exomsequenzierungsprodukte. Einige dieser Produkte müssen bei einem Gesundheitsdienstleister bestellt werden und sind möglicherweise versichert. Diese Tests werden häufig zur Diagnose von Krankheiten verwendet. Einige Unternehmen bieten den Service direkt für Tests bei Verbrauchern zu Hause an, die in von der CLIA zugelassenen und von der GAP akkreditierten Labors analysiert werden. Sie können zwar nicht als Diagnosewerkzeuge verwendet werden, können jedoch zur Beratung zu Gesundheitsdienstleistern gebracht werden.
23andMe führte ein Pilotprogramm zur Sequenzierung des gesamten Exoms durch, das im September 2011 angekündigt und 2012 eingestellt wurde. Verbraucher könnten Exomdaten zu einem Preis von 999 US-Dollar erhalten. Das Unternehmen lieferte Rohdaten und bot keine Analyse an.
- Ambry-Genetik war das erste Unternehmen, das einen Exomsequenzierungsservice für die Diagnose klinischer Krankheiten anbot. Heutzutage können Kunden Tests über Gesundheitsdienstleister bestellen, und der größte Teil der Kosten wird durch Versicherungen gedeckt.
- CircleDNA bietet zu Hause WES für 189 – 629 US-Dollar an und viele Tests beinhalten genetische Beratung. Diese Firma arbeitet auch mit DNAFit .
- Dante Labs ‚ WES startet bei 849 US-Dollar zu einem viel höheren Preis als die Konkurrenz. Dieses Unternehmen bietet auch die Sequenzierung des gesamten Genoms ab 599 US-Dollar an.
- Volles Genom bietet WES ab 525 US-Dollar an.
- GeneDx begann 2012 WES anzubieten. Ihre Preise sind variabel.
- HelixDNA bietet WES zu einem vernünftigen Preis von 145 USD plus 299 USD für eine nützliche App.
- Beide Einladung WES und Unzählige Genetik bieten diagnostische Tests an. Diese Tests sind zwar teuer, können aber durch eine Versicherung abgedeckt werden.
- Tellmegen untersucht ausgewählte Regionen des Exoms, von denen bekannt ist, dass sie mit Krankheit und Gesundheit zusammenhängen. Tests kosten 235 US-Dollar.
Sie können noch viel mehr lesen Unternehmensbewertungen auf unserem Blog und schauen Sie sich unsere Komplette Anleitung zum besten DNA-Testkit und anderen Heimtests .
